Replikacja
Informacja o budowie organizmu zawarta jest w DNA – to pewnie już wszyscy wiemy, jednak jak ta informacja jest przekazywana i wykorzystywana przez komórkę? Na to pytanie postaram się w prostych słowach odpowiedzieć w tym i kolejnych artykułach. Tym razem zajmę się wyjaśnieniem procesu replikacji.
Replikacja jest kopiowaniem materiału genetycznego w postaci DNA. Jeżeli mamy zapisaną pewną informację i chcemy się nią podzielić, musimy ją skopiować. Również komórka, gdy się dzieli, musi powielić swój DNA, aby każda z komórek potomnych otrzymała identyczną informację – identyczny zestaw genów. Kopiowanie te następuje następuje zawsze między podziałami. W przypadku eukariontów dokładnie w fazie S interfazy cyklu komórkowego.
Żeby zrozumieć jak dochodzi do replikowania DNA, musimy przypomnieć sobie jego budowę oraz sposób, w jaki geny są w nim zakodowane.
Ryc. 1. Budowa DNA
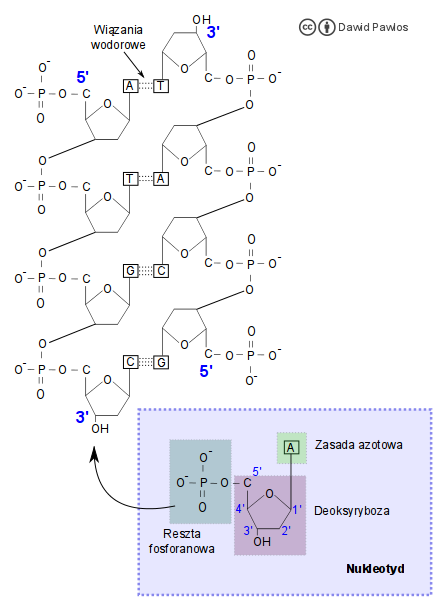
Cząsteczka DNA składa się z dwóch nici okręconych wokół siebie tworząc podwójną helisę. Każda z tych nici zbudowana jest z połączonych w odpowiedniej kolejności nukleotydów. Nukleotyd składa się z pięciowęglowego cukru – deoksyrybozy oraz dołączonych do niego reszty fosforanowej i jednej z czterech zasad azotowych: adeniny (A), tyminy (T), cytozyny (C) lub guaniny (G). Tym samym mamy cztery rodzaje nukleotydów. Jak to zostało przedstawione na ryc. 1, nukleotydy w pojedynczym łańcuchu łączą się ze sobą poprzez wiązanie kowalencyjne reszty fosforanowej jednego nukleotydu z węglem 3′ kolejnego. Oznaczenia 3′ i 5′, które widzimy na ilustracji to nic innego jak numery atomów węgla cząsteczki deoksyrybozy. Łącząc się ze sobą, nukleotydy tworzą łańcuch (jedną z nici DNA), który na swoim jednym końcu ma wolną grupę -OH przy węglu 3′, natomiast przy drugim resztę fosforanową przyłączoną do węgla 5′ cukru.
Teraz zapewne jest już jasne skąd biorą się opisywane w książkach oznaczenia końców nici DNA. Ten koniec łańcucha, na którym znajdziemy węgiel 3′ nazywamy po prostu końcem 3′, natomiast przeciwny koniec z grupą fosforanową przy piątym węglu deoksyrybozy to koniec oznaczany jako 5′. Znając te oznaczenia możemy zauważyć, że w DNA oba łańcuchy są względem siebie odwrócone – koniec 3′ jednego leży naprzeciwko końca 5′ drugiego. Mówi się o tak zwanym antyrównoległym połączeniu nici w DNA. Jak się przekonamy omawiając kolejne etapy ekspresji informacji genetycznej, jest to dosyć istotne.
Gdy spojrzymy na budowę dwuniciowej cząsteczki DNA (ryc. 1) zauważymy, że łańcuchy kwasu nukleinowego łączą się ze sobą przy pomocy wiązań wodorowych pomiędzy poszczególnymi zasadami azotowymi wchodzącymi w skład nukleotydów. Nie są to jednak wiązania całkowicie dowolne. Ze względu na budowę cząsteczki adenina (A) łączy się tylko z tyminą (T) dwoma wiązaniami wodorowymi, natomiast cytozyna tylko z guaniną trzema wiązaniami wodorowymi. Zostało to ujęte w postaci zasady komplementarności. Dzięki temu znając sekwencję zasad azotowych w jednej nici możemy określić tą sekwencję w drugiej nici. Należy tylko pamiętać o ich antyrównoległym ułożeniu w cząsteczce DNA. Mianowicie jeżeli jedna nić będzie miała sekwencję np. 5′ – ATGC – 3′, to komplementarny fragment będzie miał sekwencję: 3′ – TACG – 5′. W praktyce przyjęło się zapisywać sekwencje od końca 5′ do 3′ bez oznaczania końców jak w powyższych przykładach, dlatego w tym wypadku zapis pierwszej nici to po prostu ATGC, natomiast komplementarnej do niej to GCAT (należy odwrócić kolejność zasad, aby zacząć od końca 5′ zgodnie z konwencją).
Teraz powstaje pytanie:
jak w strukturze kwasu nukleinowego zakodować informację?
Odpowiedź jest dosyć prosta. To właśnie kolejność nukleotydów w łańcuchu DNA koduje kolejność aminokwasów w białku, a tym samym większość cech organizmu. Szczegółowy opis korelacji między DNA, a białkami wykracza jednak poza ramy tego artykułu. W tym momencie istotny jest dla nas fakt, że kopiując materiał genetyczny musimy zachować informację o kolejności nukleotydów. Najprostszym rozwiązaniem wydaje się rozplecenie podwójnej helisy i pozostawienie pojedynczych nici – na podstawie każdej z nich można przecież uzyskać tą samą informację. Jednak tylko niektórym wirusom wystarcza jedna nić DNA jako nośnik informacji. Aby utrzymać stabilność cząsteczki i zwiększyć trwałość informacji (również poprzez zachowanie kopii, która może służyć w odtworzeniu prawidłowej sekwencji zasad np. po wystąpieniu mutacji na jednej nici), konieczne jest dobudowanie drugiego, komplementarnego łańcucha.
Tak też wygląda proces replikacji. Najpierw następuje rozplecenie nici DNA, a następnie do tak powstałych wolnych, pojedynczych nici dobudowywane są komplementarne nukleotydy, które łącząc się tworzą drugą nić. Warto zauważyć, że każda z tak powstałych cząsteczek dwuniciowego DNA składa się z jednej nici starej oraz jednej nowej. Z tego względu mówi się, że jest to replikacja semikonserwatywna.
Skoro zapoznaliśmy się z samą zasadą replikacji, to czas na szczegóły związane z przebiegiem tego procesu w komórce. Otóż zachodzi on w jądrze komórkowym i organellach półautonomicznych (mitochondriach i chloroplastach) w przypadku organizmów jądrowych, bądź w cytoplazmie u prokariontów. Pozostałe różnice w całym procesie pomiędzy eukariontami i prokariontami zaznaczę w trakcie opisu jego poszczególnych etapów.
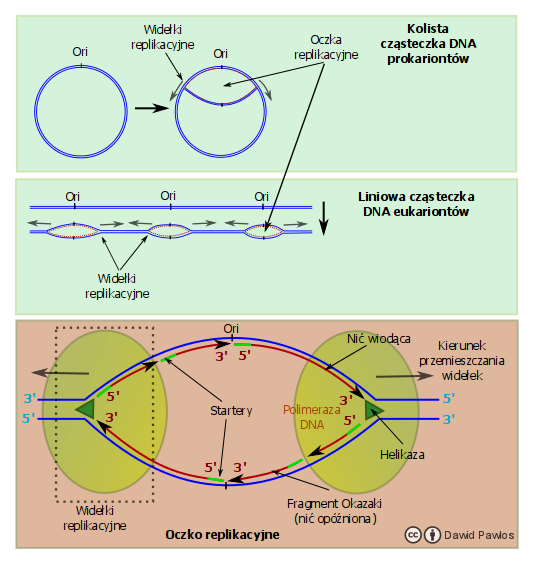
Pierwszym etapem procesu replikacji jest jego inicjacja. Polega ona na przyłączeniu się specjalnych białek do odpowiedniego miejsca na podwójnej nici DNA zwanego miejscem inicjacji replikacji (w skrócie miejsce Ori). Jedno z tych białek, zwane helikazą, rozplata podwójną helisę DNA, tak że powstaje oczko zawierające pojedyncze nici DNA (patrz ryc. 2). Do tych nici przyłącza się z kolei białko zwane polimerazą DNA, które jest enzymem katalizującym przyłączanie kolejnych, komplementarnych nukleotydów i tym samym syntezę nowej nici. Miejsce, w którym następuje rozplatanie podwójnej helisy nazywane jest widełkami replikacyjnymi. W miarę rozplatania DNA przez helikazę, widełki replikacyjne przesuwają się, a oczko się powiększa. W stronę przesuwających się widełek, po każdej z nici przesuwa się polimeraza DNA, dzięki czemu na bieżąco do nowo udostępnianych fragmentów jednoniciowego DNA dobudowywane są nukleotydy, odtwarzając brakującą nić. W przypadku prokariontów, których materiał genetyczny jest stosunkowo niewielki, występują tylko 1-2 miejsca Ori. Ponad to warto zwrócić uwagę, że DNA prokariontów w przeciwieństwie do eukariontów, jest cząsteczką kolistą. Duże cząsteczki eukariontów wymagają wielu miejsc Ori, aby cały proces replikacji nie trwał zbyt długo. W ich przypadku, inicjacja replikacji przebiega w kilku miejscach równocześnie, a tak powstałe oczka replikacyjne powiększając się łączą się ze sobą.
Wszystko było by proste, gdyby nie jeden ważny fakt: polimeraza DNA może dobudowywać nowe nukleotydy tylko do końca 3′ już utworzonego łańcucha. Co to oznacza w praktyce?
Są trzy efekty takiego działania polimerazy, które omówię w dalszej części artykułu:
Żeby zacząć syntezę nowej nici DNA, musi być najpierw utworzony tzw. starter.
Na jednej ze starych nici, której koniec 3′ leży w kierunku widełek, dobudowywanie nowej, komplementarnej nici następuje fragmentami, które dopiero później się łączą (tzw. fragmenty Okazaki).
- Skracanie końców nowych nici w cząsteczkach liniowych (nie kolistych).
Ryc. 2. Oczko replikacyjne
Starter to nic innego jak krótki fragment RNA dobudowany na zasadzie komplementarności do nici DNA stanowiącej matrycę. Startery są syntetyzowane przez enzym prymazę (z angielskiego starter to primer i stąd nazwa enzymu). W przeciwieństwie do polimerazy DNA nie potrzebuje ona już utworzonego fragmentu i może dobudowywać komplementarny łańcuch RNA do „gołej” nici DNA. Dopiero do tego krótkiego fragmentu polimeraza DNA może dobudowywać kolejne nukleotydy, tworząc dalej komplementarny łańcuch DNA. Gdy starter spełni swoją funkcję, jest usuwany przez odpowiednie enzymy (nukleazy), a na jego miejsce specjalna polimeraza DNA (inna od tej syntetyzującej większość nici) syntetyzuje brakujący fragment. Te fragmenty DNA są następnie łączone z resztą łańcucha przez ligazę.
Jak widać na ryc. 2. polimeraza syntetyzuje n o w ą n i ć od jej końca 5′ do końca 3′ (w kierunku
5′ => 3′), co biorąc pod uwagę antyrównoległe ułożenie nici w DNA oznacza, że porusza się po s t a r e j n i c i od jej końca 3′ do 5′ (w kierunku 3′ => 5′). W związku z tym powstaje pewien problem, który za chwilę opiszę. Jak to zostało ukazane na rysunku, jedna z nici DNA jest syntetyzowana ciągle, ponieważ polimeraza poruszając się zgodnie z przedstawioną wyżej zasadą (w kierunku 3′ => 5′ starej nici) zbliża się do widełek replikacyjnych i dzięki temu ma wciąż niejako „podsuwane pod nos” nowe fragmenty rozplecionego DNA. Jest to tak zwana nić wiodąca. Jej koniec 3′ znajduje się w kierunku najbliższych widełek, co jest równoznaczne z tym, jej że nić matrycowa ma przy widełkach koniec 5′. Warto zauważyć, że przy każdym z widełek replikacyjnych w oczku, synteza nici wiodącej następuje na przeciwległej nici matrycowej DNA (nawiązując do ilustracji, przy prawych widełkach będzie to górna nić, natomiast przy lewych, dolna). Problem zaczyna się gdy spojrzymy na drugą nić matrycową w widełkach. Jej koniec 5′ znajduje się do tyłu w stosunku do kierunku ruchu widełek. W tej sytuacji polimeraza musi syntetyzować nowy łańcuch DNA w kierunku przeciwnym do ruchu widełek (bo może poruszać się tylko w kierunku 3′ => 5′ starej nici), a co za tym idzie każdy nowy fragment rozplecionej matrycy wymaga osobnego startera, aby polimeraza DNA dobudowała do niego kolejny fragment komplementarnego łańcucha. Z tego względu nowa nić składa się początkowo z odcinków, które na cześć ich odkrywcy nazwano fragmentami Okazaki, sam zaś tak syntetyzowany łańcuch DNA określa się mianem nici opóźnionej. Każdy fragment Okazaki posiada swój własny starter (polimeraza za każdym razem, gdy rozpleciony zostanie nowy fragment DNA, musi zaczynać niejako od nowa).
Startery są usuwane i zastępowane przez DNA, jak opisano to wcześniej, po czym fragmenty łączone są przez ligazę, tworząc ciągły łańcuch nici opóźnionej.
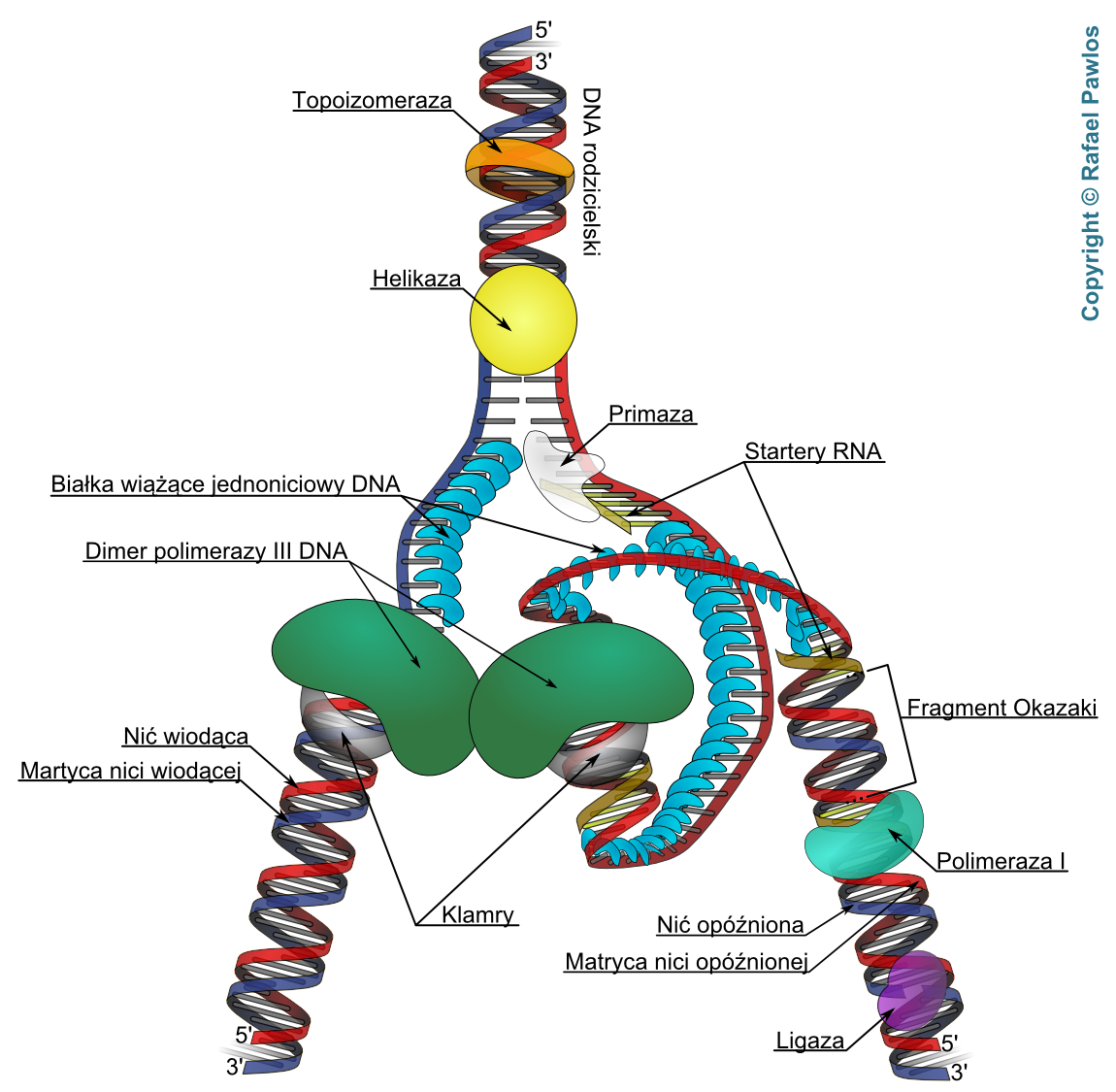
Ryc. 3. Widełki replikacyjne
Powyższy opis jest nieco uproszczony, jednak wystarczający, aby zrozumieć zasadę całego procesu. Osobom lubiącym szczegóły i pragnącym lepiej zrozumieć pewne aspekty, proponuję analizę ryc. 3. Przedstawia ona sytuację najbliższą prawdy. Jak widać sama polimeraza DNA jest dimerem, co oznacza, że składa się z dwóch połączonych ze sobą, funkcjonalnych białkowych enzymów, z których każdy prowadzi syntezę na oddzielnej nici rozplecionego DNA. Przedstawiony schemat został opracowany na podstawie badań na bakterii E. coli. U eukariontów w replikacji biorą udział inne polimerazy. Oznaczone na ilustracji białka wiążące jednoniciowy DNA zapobiegają ponownemu splataniu się pojedynczych nici, natomiast klamry doczepione do polimerazy, utrzymują ją przy łańcuchu DNA. Istotne na schemacie jest zapętlenie tworzące się na nici opóźnionej. Dzięki niemu polimeraza DNA nie musi się cofać od widełek replikacyjnych, aby syntetyzować fragment Okazaki. Zapętlony fragment nici opóźnionej ma koniec 5′ skierowany w stronę widełek replikacyjnych. Po dotarciu polimerazy wzdłuż matrycy (nici opóźnionej) do startera poprzedniego, już zsyntetyzowanego fragmentu Okazaki, polimeraza odłącza się od matrycy i przyłącza ponownie w miejscu kolejnego startera (na rysunku bliżej widełek), tworząc nowe zapętlenie. Ciekawą animację przedstawiającą jak to wygląda można znaleźć tutaj [link: http://www.youtube.com/watch?feature=player_embedded&v=OjPcT1uUZiE#t=103s].
Oznaczony na schemacie enzym o nazwie topoizomeraza usuwa naprężenia powstające podczas rozplatania podwójnej helisy. Można zrozumieć o co chodzi, gdy wyobrazimy sobie, że powiększyliśmy DNA do rozmiarów kilkumetrowego sznurka i chcemy go rozplątać pociągając za dwie nici wchodzące w jego skład. Łatwo się domyślić, że w tej sytuacji fragment, który rozplatamy, będzie coraz bardziej się zaciskał, przez powstawanie dodatkowych skrętów podwójnej helisy. Jednym ze sposobów pozbycia się ich i umożliwienia dalszego rozplatania nici jest przecięcie jednej z nich, albo obu. Umożliwi to rozkręcenie się nadmiernie skręconej helisy i to właśnie robi topoizomeraza: przecina jedną z nici, a po okręceniu się DNA wokół własnej osi i zniwelowaniu naprężeń, łączy przecięte nici z powrotem. Nie jest to bynajmniej jedyna funkcja tego enzymu, jednak tym razem nie będę się w to szczegółowo zagłębiał.
Ryc. 4. Telomery i telomeraza
Istnieje także kwestia skracania cząsteczek DNA podczas kolejnych replikacji. Wynika to z tego, że po zreplikowaniu całej liniowej cząsteczki DNA, należy jeszcze usunąć startery. Jednak co z lukami powstałymi po starterach, które znajdowały się na końcu nici? Przecież po usunięciu startera z końca nici, polimeraza nie może uzupełnić luki, ponieważ jak już wiemy, może dobudowywać nukleotydy tylko do już istniejącego końca 3′, a więc potrzebowałaby dodatkowego startera przed tą luką (ryc. 4). Niestety to już jest koniec nici i dodatkowego startera nie ma na czym zsyntetyzować, więc dziura zostaje. Gdy weźmiemy pod uwagę fakt, że w trakcie kolejnej replikacji skrócona nić będzie pełniła funkcję matrycy do dobudowania nici komplementarnej, która z kolei znowu ulegnie skróceniu, sytuacja może wydać się niepokojąca. Przecież w ten sposób w kolejnych rundach replikacji cząsteczki DNA stają się coraz krótsze, a więc tracona jest część kodu z ich końca. Na szczęście istnieją mechanizmy zapobiegające utracie informacji w ten sposób. Pierwszy z nich opiera się na tym, że na końcach liniowych cząsteczek DNA znajdują się tzw. sekwencje telomerowe, czyli wiele powtórzeń krótkich sekwencji nukleotydów, które nic nie kodują, a więc ich utrata nie wpłynie negatywnie na komórkę. Końce DNA, a więc również końcówki
chromosomów, które są przecież upakowaną formą tego kwasu nukleinowego, nazywamy telomerami. Można się domyślić, że jednak przy wielu podziałach komórki (a tym samym wielu replikacjach) telomery będą się skracać, aż znikną zupełnie i wtedy kolejne podziały wiązałyby się z utratą genów leżących w pobliżu końca cząsteczki DNA. Tak też dzieje się w większości komórek ludzkiego organizmu. Po dokonaniu pewnej liczby podziałów dalej się nie dzielą. Dla większości komórek ludzkich ustalono, że w sprzyjających warunkach mogą się podzielić maksymalnie około 50 razy. Liczbę tą na cześć odkrywcy określono mianem limitu Hayflicka.
Jednak jak zaznaczyłem, tak zachowuje się większość komórek, ale nie wszystkie. Część z nich może dzielić się w nieskończoność, a ich telomery nie skracają się. Należą do nich szeroko pojęte komórki macierzyste oraz nowotworowe. W przypadku tych pierwszych muszą one nieustannie się dzielić, aby np. odtwarzać złuszczający się naskórek, zużywające się krwinki, czy brać udział w naprawianiu uszkodzeń. Termin komórki macierzyste użyty został tu dość ogólnikowo i nieprecyzyjnie, jednak byłby to temat na osobny artykuł. Co się dzieje, że w komórkach tych nie następuje skracanie telomerów? Kluczem jest tu specjalny enzym, który posiadają. Nazwany został telomerazą, a jego funkcja polega na wydłużaniu telomerów po każdej replikacji. Specyfika tego enzymu polega na tym, że składa się z białka oraz krótkiej cząsteczki RNA, która wyjątkowo pełni funkcję matrycy do syntezy DNA. Jak widzimy na ryc. 6. telomeraza nie wydłuża bezpośrednio nowej nici, lecz wydłuża starą nić, dając niejako podstawę do syntezy nowego startera i wydłużenia nowej nici. Ostatecznie nowa nić nadal zostaje krótsza od starej, jednak tym razem obie nici są dłuższe niż normalnie, a więc telomery się nie skracają. Warto zauważyć, że w przypadku prokariontów posiadających koliste cząsteczki DNA problem skracania telomerów nie występuje.
Pozostaje jeszcze jedno zagadnienie dotyczące polimerazy DNA, a mianowicie jej zdolność do poprawiania błędów. Wiadomo, że tak ważny element jakim jest materiał genetyczny powinien być skopiowany z jak największą precyzją, ponieważ każdy błąd (czyli w tym wypadku mutacja) może doprowadzić do syntezy nieprawidłowego lub w ogóle braku syntezy białka, a to z kolei może prowadzić do utraty funkcji komórki bądź jej śmierci. Dlatego już sama polimeraza potrafi wykrywać i poprawiać błędnie wstawione nukleotydy. Po każdym wstawieniu nowego nukleotydu polimeraza sprawdza, czy jest on komplementarny do nukleotydu na nici matrycowej. Jeżeli przypadkowo został przyłączony nukleotyd nie pasujący do tego miejsca, polimeraza korzysta ze swojej aktywności egzonukleazowej, wycina błędny nukleotyd i wstawia w jego miejsce prawidłowy. Mówi się, że polimeraza posiada aktywność egzonukleazy w kierunku 5′ => 3′ co oznacza, że potrafi wycinać nukleotydy od końca nici, którą już zsyntetyzowała (wstecz). Nawet pomimo tej właściwości polimerazy, błędy podczas replikacji zdarzają się, jednak niezwykle rzadko (około 1 błędnie wstawiony nukleotyd na miliard).
Na zakończenie chciałbym także zwrócić uwagę na jeden istotny fakt. Otóż mamy tu do czynienia z procesem anabolicznym (następuje synteza łańcucha polinukleotydowego), a więc do jego realizacji potrzebna jest energia. Jak wiemy, głównym magazynem energii w komórce jest ATP. ATP to nic innego jak nukleotyd adeninowy z dołączonymi dodatkowo dwoma resztami fosforanowymi (czyli trifosforan nukleozydu adeninowego – dla przypomnienia nukleotyd to nukleozyd + 1 reszta fosforanowa). W trifosforanie nukleozydu są 2 wiązania wysokoenergetyczne, których rozerwanie dostarcza energii. Wbrew pozorom cała energia potrzebna do procesu replikacji nie pochodzi bezpośrednio z ATP. Przecież do syntezy komplementarnego łańcucha również wykorzystywane są trifosforany pozostałych nukleozydów, a więc CTP, GTP, i TTP. Odłączanie dodatkowych dwóch reszt fosforanowych od tych związków daje nukleotyd dobudowywany do łańcucha, dwie wolne reszty fosforanowe i energię potrzebną do stworzenia wiązania kowalencyjnego łączącego resztę fosforanową nowego nukleotydu z węglem 3′ wydłużanego łańcucha. Teraz już zapewne jest jasne, że podczas syntezy DNA nie potrzeba dodatkowych nośników energii, ponieważ same substraty, czyli trifosforany nukleozydów (lub inaczej difosforany nukleotydów), stanowią związki wysokoenergetyczne dostarczające energię do syntezy.
Podsumowując przedstawione wyżej informacje na temat replikacji możemy powiedzieć że:
1. Replikacja zachodzi w jądrze komórkowym i organellach półautonomicznych u eukariontów lub w cytoplazmie u prokariontów i zachodzi zawsze przed podziałem komórki w celu przekazania kopii informacji genetycznej komórkom potomnym.
2. Replikacja jest procesem semikonserwatywnym, w którym biorą udział takie białka jak helikaza DNA, prymaza, dwa typy polimerazy DNA, nukleazy oraz ligaza.
3. Replikacja rozpoczyna się w miejscach Ori na DNA, przy czym u prokariontów tych miejsc jest 1-2 na jednej cząsteczce DNA, natomiast u eukariontów jest ich wiele. W miejscu Ori helikaza rozplata podwójną helisę, prymaza syntetyzuje startery, a polimeraza DNA przyłącza kolejne nukleotydy, syntetyzując łańcuch komplementarny do starej nici. Startery RNA są następnie zastępowane przez DNA dzięki aktywności nukleaz, polimerazy DNA i ligazy.
4. Polimeraza porusza się w stronę widełek replikacyjnych, w kierunku 3′ => 5′ starej nici, syntetyzując nową nić w kierunku 5′ => 3′ (dobudowuje nukleotydy do końca 3′). W związku z tym możemy wyróżnić nić wiodącą, na której synteza następuje w sposób ciągły, zgodnie z ruchem widełek oraz nić opóźnioną, na której syntetyzowane fragmenty Okazaki, które dopiero później się łączą.
5.Usuwanie starterów powoduje skracanie telomerów w większości komórek. Tylko komórki stale dzielące się, takie jak komórki macierzyste lub nowotworowe, posiadają enzym telomerazę odpowiedzialny za wydłużanie telomerów.
6.Polimeraza DNA posiada aktywność egzonukleolityczną, dzięki której może wycinać błędnie wstawione przez siebie nukleotydy i wymieniać je na prawidłowe, co zapobiega wielu mutacjom i zwiększa wierność powstałej kopii DNA.
7. Energia do syntezy DNA pochodzi z rozpadu wiązań wysokoenergetycznych między resztami fosforanowymi trifosforanów nukleozydów, które są substratami tej reakcji.
To wszystko na co chciałem zwrócić uwagę w tym miejscu.
Literatura:
1. Praca zbiorowa pod redakcją Ewy Bartnik i Waldemara Lewińskiego: Biologia – zakres rozszerzony; cz. 3. Wyd. Operon, 2005r.
2. Eldra P. Salomon, Linda R. Berg, Diana W. Martin: Biologia – według wydania VII amerykańskiego; Oficyna wydawnicza Multico, 2007r.
Dawid Pawlos
CZY TEN ARTYKUŁ OKAZAŁ SIĘ POMOCNY? MASZ DODATKOWE SUGESTIE ALBO PYTANIA? NAPISZ DO NAS! A MOŻE CHCESZ TEŻ O CZYMŚ NAPISAĆ I OPUBLIKOWAĆ? DOŁĄCZ DO NAS! REDAKCJA@BIOMIST.PL

dziekuje że w koncu ktos wyjasnił "po chłopsku" jak myka i w ktorą strone polimeraza po nici :')
bardzo pomocny artykuł, dzięki! 😉
świetny artykuł uzupełniający wszystkie ubytki wiedzy szkolnej 🙂